シングルセル(1細胞)遺伝子発現解析とは
シングルセル(1細胞)遺伝子発現解析とは、従来のように細胞集団(バルク)として平均的に解析する方法とは異なり、単離した1細胞ごとに遺伝子発現を解析する手法です。これにより、同一組織内に存在する細胞の多様性や不均一性を明らかにすることができます。
バルク解析では捉えにくかった、がん組織における多様な細胞集団や免疫環境の解析も可能となり、がん治療や免疫療法への応用が期待されています。
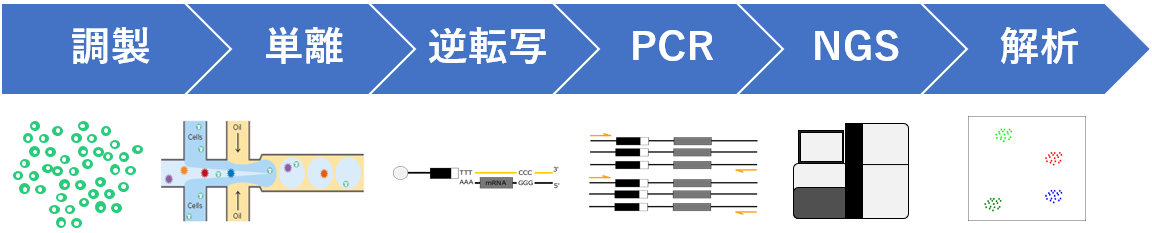
シングルセル解析は現在、さまざまなプラットフォームが開発されており、研究目的やサンプル特性、予算に応じて最適な手法を選択することが重要です。基本的な解析プロセスは共通しており、以下にその概要を示します。
細胞などのサンプル懸濁液調製
シングルセル解析では、解析対象となる組織や試料から、単一細胞または単一核が均一に分散したサンプル懸濁液を調製します。組織、血液、生検体、腫瘍、培養細胞、植物片、真菌類(酵母など)など、さまざまな試料に対応可能です。
このサンプル懸濁液調製工程は、後続の単離や遺伝子発現解析の品質に影響するため、細胞の生存率や凝集の有無に注意して行うことが重要です。
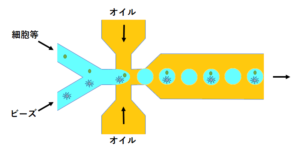
単離・mRNA捕捉(ドロップレット式の場合)
シングルセル(1細胞)をドロップレットやウェルなどの微小区画に分配し、個別バーコード配列を有するmRNA捕捉粒子と1細胞ずつペアリングして単離します。
ドロップレット方式では、区画はドロップレットジェネレーターによって生成され、細胞とmRNA捕捉粒子が制御された条件下で封入されます。この際、1区画に複数細胞が入る確率(ダブレット率)は解析精度に影響するため、同一投入細胞数条件でのダブレット率比較が重要です。
細胞溶解液はmRNA捕捉粒子と同一溶液として用意され、細胞はドロップレット内で初めて接触することで、区画形成と同時に細胞溶解およびmRNA捕捉が開始されます。
逆転写・cDNA合成
バーコード(識別)配列およびユニーク分子識別子(UMI)が付加されたmRNAを鋳型として、逆転写酵素を用いた逆転写反応を行い、cDNA(相補的DNA)の第1鎖を合成します。この工程では、mRNAに付加されていた細胞バーコードやUMI情報がcDNAへと引き継がれるため、後の解析において、どの細胞由来の遺伝子発現であるかを識別することが可能になります。
逆転写/cDNA合成は、RNA情報を安定で増幅可能なDNA情報へ変換する重要な工程であり、以降のライブラリー調製および次世代シーケンシング解析の基盤となります。
PCR増幅・品質評価・ライブラリー調製
合成されたcDNAを鋳型としてPCRにより増幅し、NGS解析に必要なDNA量を確保します。この工程では、後続解析に適したcDNA断片を十分な量で得ることが目的となります。
増幅産物は、電気泳動やフラグメント解析などにより、サイズ分布や増幅状態を確認します。これにより、非特異的な増幅や過度な断片化が起きていないかを評価します。
品質が確認されたPCR産物は、NGS用キットを用いてライブラリー調製を行い、シーケンシングに必要なアダプター配列やインデックス配列を付加します。NGS解析はコストを要するため、品質が十分に確認されたサンプルのみを次工程へ進めることが重要です。
NGS(次世代シーケンシング)

ライブラリー調製されたDNAを用いて、Illumina社の次世代シーケンサーによる配列解析を行います。シングルセルRNA解析では、解析規模や目的に応じて NextSeq 1000/2000やNovaSeq Xシリーズなどのプラットフォームが用いられます。
得られたリード配列には細胞バーコードおよびUMI情報が含まれており、これらをもとに細胞ごとの遺伝子発現情報を再構築することが可能です。NGS工程は、最終的なデータ品質に大きく影響する重要なステップです。
シングルセルデータ解析

シングルセル解析では、NGSデータから得られた遺伝子発現情報をもとに、段階的なデータ処理と解析を行います。一次解析により細胞ごとの発現量データを整備した後、品質管理や正規化などを通じて、解析に適したデータセットを構築します。
その後、次元削減やクラスタリング解析を用いて、遺伝子発現パターンが類似した細胞集団を同定します。これらの結果はUMAPやt-SNEなどの可視化手法によって表現され、細胞間の関係性や集団構造を直感的に把握することが可能です。
最終的には、クラスタごとの特徴的な遺伝子発現を手がかりとして、細胞タイプや状態の違いを解釈し、条件依存的な変化や生物学的な多様性の理解へとつなげていきます。
参考文献
- Brower, Kara K et al. “Double emulsion flow cytometry with high-throughput single droplet isolation and nucleic acid recovery.” Lab on a chip vol. 20,12 (2020): 2062-2074. doi:10.1039/d0lc00261e
- Gross, Andre et al. “Technologies for Single-Cell Isolation.” International journal of molecular sciences vol. 16,8 16897-919. 24 Jul. 2015, doi:10.3390/ijms160816897
- Islam S, Zeisel A, Joost S, et al. Quantitative single-cell RNA-seq with unique molecular identifiers. Nat Methods. 2014;11(2):163-166. doi:10.1038/nmeth.2772
- Klein AM, Mazutis L, Akartuna I, et al. Droplet barcoding for single-cell transcriptomics applied to embryonic stem cells. Cell. 2015;161(5):1187-1201. doi:10.1016/j.cell.2015.04.044
- Macosko EZ, Basu A, Satija R, et al. Highly parallel genome-wide expression profiling of individual cells using nanoliter droplets. Cell. 2015;161(5):1202-1214. doi:10.1016/j.cell.2015.05.002
- Melsted P, Ntranos V, Pachter L. The barcode, UMI, set format and BUStools. Bioinformatics. 2019;35(21):4472-4473. doi:10.1093/bioinformatics/btz279
- Nguyen, Quy H et al. “Experimental Considerations for Single-Cell RNA Sequencing Approaches.” Frontiers in cell and developmental biology vol. 6 108. 4 Sep. 2018, doi:10.3389/fcell.2018.00108
- Valihrach, Lukas et al. “Platforms for Single-Cell Collection and Analysis.” International journal of molecular sciences vol. 19,3 807. 11 Mar. 2018, doi:10.3390/ijms19030807
- Zheng GX, Terry JM, Belgrader P, et al. Massively parallel digital transcriptional profiling of single cells. Nat Commun. 2017;8:14049. doi:10.1038/ncomms14049

NTサイエンスへのお問い合わせ内容には、通常2営業日以内にご返信致します。
※装置や特注品の御見積は、通常よりもお時間を要する場合がありますので、予めご了承ください。
旧来の050IP電話番号廃止のお知らせ:
事業者のサービス終了に伴い、050-5539で始まる番号は2025年3月31日をもって廃止となりました。
製品お問い合わせや見積依頼は下記お問い合わせフォーム、メール又はFAXにてお願い致します。
ご回答以外の不要な営業アプローチをすることはありませんのでお気軽にお問い合わせください。
◆お問い合わせフォーム
※営業・セールス、スパム、迷惑行為は禁止です。
その他連絡先
◆メール
![]()
※営業・セールス、スパム、迷惑行為は禁止です。
※nt-science.com からのメールをブロック解除し、迷惑メールフォルダをご確認ください。
◆FAX
![]()
※当日受注分:平日17:30まで(土日祝日、休業期間を除く)